Creo que es un buen momento para hacer un primer ejemplo de aprendizaje automático. Implementaremos un modelo de regresión lineal simple, el modelo más sencillo, con Python. Vamos a desarrollarlo de dos formas. La primera será, como me dijo alguien hace poco, con cincel y martillo, esto es, con python puro. La segunda será utilizando la librería scikit-learn.
El objetivo de implementar un modelo estadístico es intentar explicar el comportamiento de una variable a partir de los datos de otras variables. A la variable objeto de estudio se la denomina variable de salida o de respuesta. A las variables que nos ayudarán en el estudio se las llama variables de entrada, explicativas o predictoras.
La función de regresión más sencilla es la lineal. Y dentro de ésta, la simple. Se llama así porque sólo vamos a disponer de una variable de entrada o explicativa. Este modelo es una aproximación muy simple al aprendizaje supervisado. Con él comprobaremos si existe una relación entre la variable de entrada y la de salida, e intentaremos predecir el valor de la variable de salida en función de nuestra variable de entrada.
El modelo matemático para una regresión lineal se puede escribir así:
![]()
que en nuestro caso se reduciría a:
![]()
donde
- x : variable de entrada.
- a : término independiente (intercept). Valor de y cuando x es nulo.
- b : pendiente de la recta (slope). Cuánto crece y cuando x sufre un cambio.
- y : variable de salida.
- ε : error.
Tenemos que estimar dicha recta de regresión, o, lo que es lo mismo, estimar los coeficientes a y b. El objetivo final es encontrar una recta en la que la distancia vertical de los datos a dicha recta sea mínima. Para ello vamos a emplear el método más popular, la estimación por mínimos cuadrados. Éste método fue obra de un auténtico crack, Carl Friedrich Gauss. Consiste en calcular los parámetros a y b tales que hagan mínima la suma de los cuadrados de las distancias entre los valores observados y los valores estimados. A la diferencia entre el valor del dato y la predicción se le llama residuo.
Al final del desarrollo por mínimos cuadrados, se obtienen una expresión para cada uno de los coeficiente:
![]()
![]()
![]()
Así que vamos a empezar a escribir nuestro código. Como siempre, lo primero son los datos. Aquí podéis descargar los datos que vamos a utilizar, un csv con datos de potencia eléctrica de climatización y temperatura exterior de una planta, durante el mes de agosto.
Cincel y martillo
1.- Importamos las librerías necesarias y obtenemos los datos
import pandas as pd import numpy as np import matplotlib.pyplot as plt import seaborn as sns import random import math import csv
Abrimos el archivo y creamos una lista para cada columna.
with open('data_LR.csv', 'r') as f:
reader = csv.reader(f, delimiter='|')
OUTDOOR_TEMP = []
ELECTRIC_POWER = []
for index, row in enumerate(reader):
if index == 0:
header = row
else:
try:
outNum = float(row[0].replace(",", "."))
except:
outNum = None
OUTDOOR_TEMP.append(outNum)
try:
elecNum = float(row[1].replace(",", "."))
except:
elecNum = None
ELECTRIC_POWER.append(elecNum)
2.- Echamos un vistazo a los datos.
Para ello, he hecho una función que devuelve un diccionario donde las claves son las columnas. Los valores de éstas columnas son otro diccionario donde las claves y los valores son los correspondientes a el número de registros, las clases de datos, el número de valores nulos, la media, la desviación típica, el máximo y el mínimo.
def info(header, data_list):
"""
:param header: lista con los encabezados de las columnas
:param data_list: lista con las listas de datos de las columnas: [lista1, lista2, etc...]
:return: diccionario de diccionarios con número de registros, tipo de dato, número de na,
media, std, min, max de cada columna.
"""
from collections import defaultdict
header = header
columns = data_list
values = defaultdict()
for index, head in enumerate(header):
aux = defaultdict()
aux['len'] = len(columns[index])
aux['clases'] = set([type(ele) for ele in columns[index]])
aux['na'] = sum(1 for ele in columns[index] if ele == None)
# media
media = sum(ele for ele in columns[index] if ele != None) / len(columns[index])
aux['media'] = media
# std
n = sum(1 for ele in columns[index] if ele != None)
std = ((1 / (n - 1)) * sum((ele - media) ** 2 for ele in columns[index] if ele != None)) ** 0.5
aux['std'] = std
# minimo
aux['min'] = min(ele for ele in columns[index] if ele != None)
# maximo
aux['max'] = max(ele for ele in columns[index] if ele != None)
values[head] = aux
return values
print('_'*60 + 'COLUMNS')
print (header)
____________________________________________________________COLUMNS ['OUTDOOR_TEMP', 'ELECTRIC_POWER']
Vamos a usar nuestra función info:
print ('_'*60 + 'INFO') print (info(header, [OUTDOOR_TEMP, ELECTRIC_POWER]))
defaultdict(None,
{'ELECTRIC_POWER': defaultdict(None,
{'clases': {NoneType, float},
'len': 1496,
'max': 391.71,
'media': 285.83182486631,
'min': 0.0,
'na': 2,
'std': 41.51823016424719}),
'OUTDOOR_TEMP': defaultdict(None,
{'clases': {float},
'len': 1496,
'max': 38.310135,
'media': 28.544429085561454,
'min': 0.0,
'na': 0,
'std': 6.364374947698145})})
El resultado nos muestra que en la columna ELECTRIC_POWER hay dos valores nulos. Los eliminamos:
#Quitamos los nas index_to_drop = [index for index, val in enumerate(ELECTRIC_POWER) if val is None] ELECTRIC_POWER = [val for index, val in enumerate(ELECTRIC_POWER) if index not in index_to_drop] OUTDOOR_TEMP = [val for index, val in enumerate(OUTDOOR_TEMP) if index not in index_to_drop]
print (info(header, [OUTDOOR_TEMP, ELECTRIC_POWER]))
defaultdict(None,
{'ELECTRIC_POWER': defaultdict(None,
{'clases': {float},
'len': 1494,
'max': 391.71,
'media': 286.21446452476556,
'min': 0.0,
'na': 0,
'std': 41.51646570695531}),
'OUTDOOR_TEMP': defaultdict(None,
{'clases': {float},
'len': 1494,
'max': 38.310135,
'media': 28.54050408902272,
'min': 0.0,
'na': 0,
'std': 6.36757237847448})})
3.- Exploramos los datos.
def visual(header, X, y):
"""
:param header: Lista con los nombres de los encabezados
:param X: Lista con los valores de la columna a colocar en el eje X
:param y: Lista con los valores de la columna a colocar en el eje y
:return: matplotlib figure plot
"""
fs = 10 # fontsize
fig, axs = plt.subplots(3, 2, figsize=(6, 6))
plt.subplots_adjust(top=0.9, bottom=0.1, hspace=0.5, wspace=0.2, left=0.125, right=0.9)
axs[0, 0].scatter(X, y, c='r', edgecolors=(0, 0, 0), alpha=0.2)
axs[0, 0].set_title('Scatter %s vs %s' %(header[1], header[0]), fontsize=fs)
axs[1, 0].hist(X, color='red')
axs[1, 0].set_title('Hist %s' %header[0], fontsize=fs)
axs[0, 1].hist2d(X, y)
axs[0, 1].set_title('Hist 2D', fontsize=fs)
axs[1, 1].hist(y, color='blue')
axs[1, 1].set_title('Hist %s' %header[1], fontsize=fs)
axs[2, 0].boxplot(X)
axs[2, 0].set_title('Box %s' %header[0], fontsize=fs)
axs[2, 1].boxplot(y)
axs[2, 1].set_title('Box %s' %header[1], fontsize=fs)
plt.show()
#Ploteamos la gráfica visual(header, OUTDOOR_TEMP, ELECTRIC_POWER)
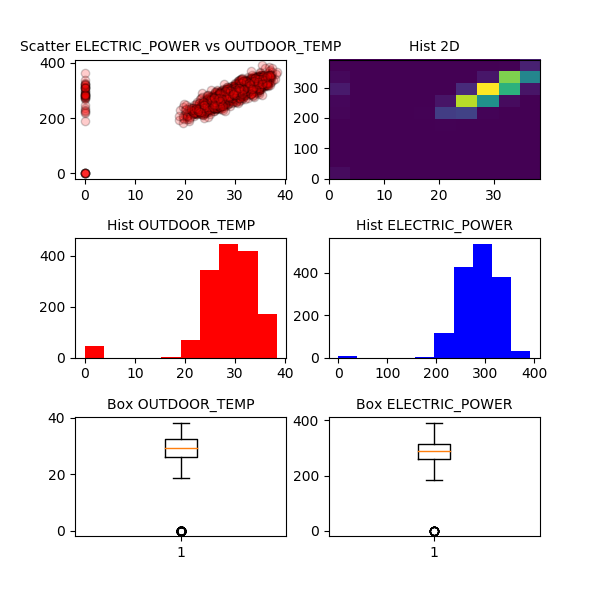 En la info podemos ver que los valores mínimos en ambos campos son cero. Estos valores son atípicos (outliers), ya que la planta se encuentra en Madrid y en agosto es imposible que la temperatura baje tanto. Gráficamente queda claro que los valores cero en ambas columnas son valores atípicos. Los eliminamos.
En la info podemos ver que los valores mínimos en ambos campos son cero. Estos valores son atípicos (outliers), ya que la planta se encuentra en Madrid y en agosto es imposible que la temperatura baje tanto. Gráficamente queda claro que los valores cero en ambas columnas son valores atípicos. Los eliminamos.
#Quitamos los outlier o valores atípicos index_to_drop = [index for index, val in enumerate(OUTDOOR_TEMP) if val == 0] ELECTRIC_POWER = [val for index, val in enumerate(ELECTRIC_POWER) if index not in index_to_drop] OUTDOOR_TEMP = [val for index, val in enumerate(OUTDOOR_TEMP) if index not in index_to_drop]
print (info(header, [OUTDOOR_TEMP, ELECTRIC_POWER]))
defaultdict(None,
{'ELECTRIC_POWER': defaultdict(None,
{'clases': {float},
'len': 1449,
'max': 391.71,
'media': 287.81427881297435,
'min': 183.12,
'na': 0,
'std': 35.88844333632387}),
'OUTDOOR_TEMP': defaultdict(None,
{'clases': {float},
'len': 1449,
'max': 38.310135,
'media': 29.42685514768802,
'min': 18.765305,
'na': 0,
'std': 3.963016838173277})})
visual(header, OUTDOOR_TEMP, ELECTRIC_POWER)
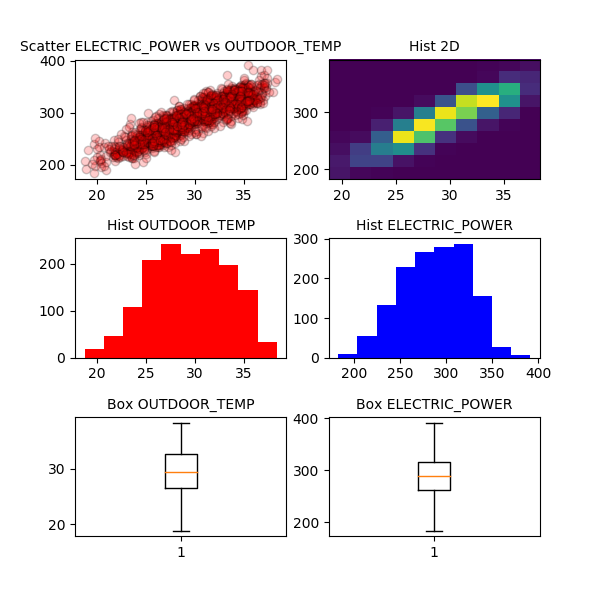
Con la gráfica de la izquierda de la primeras fila podemos aventurar que existe una relación lineal entre la temperatura exterior y la potencia de climatización de la planta.
4 .- Creamos los datos de entrenamiento y testeo.
#Creamos las listas para training y test aleatoriamente all_data = [[x_val, y_val] for x_val, y_val in zip(OUTDOOR_TEMP, ELECTRIC_POWER)] print (all_data[:5]) random.shuffle(all_data) div = math.ceil(len(all_data)*0.3) data_train = all_data[:div] data_test = all_data[div:] data_train_X = [ele[0] for ele in data_train] data_train_y = [ele[1] for ele in data_train] data_test_X = [ele[0] for ele in data_test] data_test_y = [ele[1] for ele in data_test]
5.- Creamos el modelo y lo entrenamos.
Bueno, pues ahora vamos a construir nuestro modelo. Creamos una clase que llamaremos Lin_reg.
class Lin_reg():
def __init__(self, X, Y):
"""
:param X: lista con los valores de la variable de las abscisas
:param y: lista con los valores de la variable de las ordenadas
"""
self.X = X
self.y = Y
self.N = len(self.X)
self.X_mean = sum(self.X) / len(self.X)
self.y_mean = sum(self.y) / len(self.y)
self.X_std = (1 / (self.N - 1) * sum((ele - self.X_mean) ** 2
for ele in self.X)) ** 0.5
self.y_std = (1 / (self.N - 1) * sum((ele - self.y_mean) ** 2
for ele in self.y)) ** 0.5
self.X_var = self.X_std ** 2
self.y_var = self.y_std ** 2
self.cov = sum([i * j for (i, j) in zip([ele - self.X_mean for ele in self.X],
[ele - self.y_mean for ele in self.y])]) / (self.N)
self.r = self.cov / (self.X_std * self.y_std)
def Coeficientes(self):
if len(self.X) != len(self.y):
raise ValueError('unequal length')
self.b = self.cov / self.X_var
self.a = self.y_mean - (self.b * self.X_mean)
return self.a, self.b
def predict(self, X):
yp = []
for x in X:
yp.append(self.a + self.b * x)
return yp
Creamos una instancia de la clase pasándola los datos de entrenamiento
mylinreg=Lin_reg(data_train_X,data_train_y)
y le pedimos al modelo los coeficientes de la recta de regresión
a, b = mylinreg.Coeficientes()
print('La recta de regresión es: y = %f + %f * X'%(mylinreg.Coeficientes()))
print('El coeficiente de correlación es: r = %f' %mylinreg.r)
La recta de regresión es: y = 48.043482 + 8.153666 * X El coeficiente de correlación es: r = 0.895353
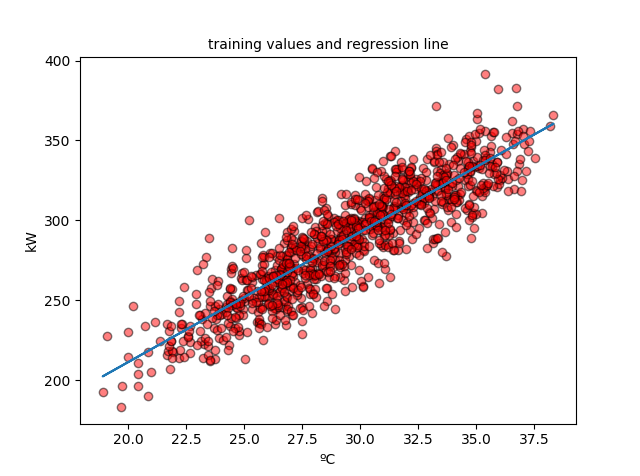
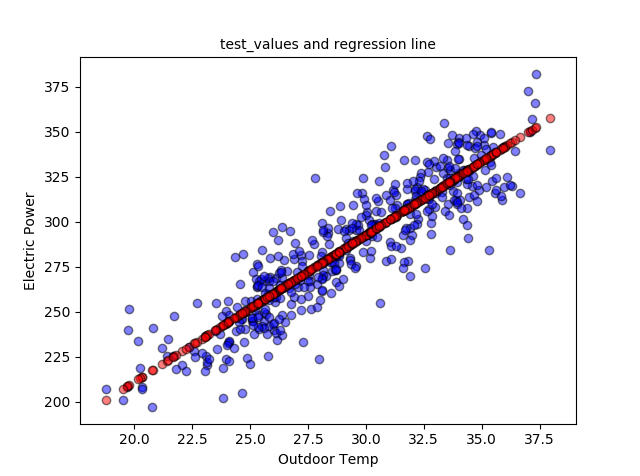
Dibujamos los datos de entrenamiento y la recta de regresión:
plt.scatter(data_train_X, data_train_y, c='r', edgecolors=(0, 0, 0), alpha=0.5) plt.plot(data_train_X, [a + b * x for x in data_train_X]) plt.show()
6.- Hacemos la predicción con los datos de test.
predictions = mylinreg.predict(data_test_X)
Podemos dibujar los datos de test con los datos predichos:
plt.scatter(data_test_y, predictions, c='r', edgecolors=(0, 0, 0), alpha=0.5)
plt.title('predicted values vs real values', fontsize=10)
plt.xlabel('real values')
plt.ylabel('predicted values')
plt.show()
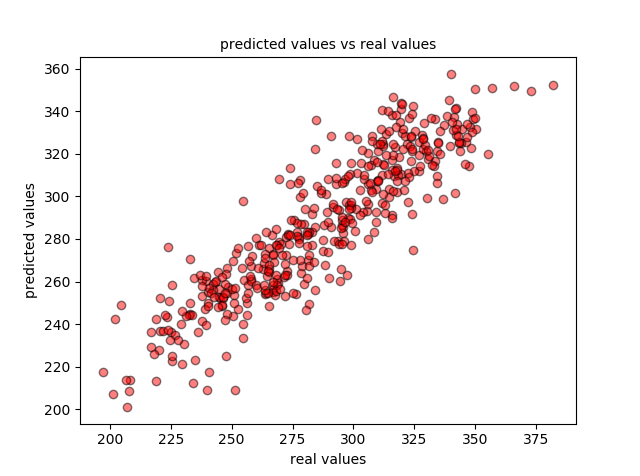
y también los datos de test con la recta de regresión:
7.- Evaluación del modelo.
Para la evaluación del modelo vamos a calcular algunas métricas que luego compararemos con el modelo realizado con scikit-learn. Los indicadores de desviación que vamos a calcular son:
![Rendered by QuickLaTeX.com \[ \begin{aligned} \underline{\textbf{Mean Error}}: ME = \frac{\sum_{i=1}^n (y - \hat{y})}{n}\\ \underline{\textbf{Mean Absolute Error}}: MAE = \frac{\sum_{i=1}^n |y - \hat{y}|}{n}\\ \underline{\textbf{Mean Square Error}}: MSE = \frac{\sum_{i=1}^n (y - \hat{y})^{2} }{n}\\ \underline{\textbf{Root Mean Square Error}}: RMSE = \sqrt{MSE}\\ \underline{\textbf{Standard Deviation of Residuals}}: SDR = \sqrt{\frac{ 1}{n-1}\sum_{i=1}^n (y - \hat{y})^{2}}\\ \end{aligned} \]](https://koldopina.com/wp-content/ql-cache/quicklatex.com-80e6dd04357cf8a90ba75257f45d60f1_l3.png)
#Metricas
#Mean Error - Desviación media
ME = sum(y_pred - y_test for y_pred, y_test in zip(predictions,data_test_y)) / len(predictions)
#Mean Absolute Error (error absoluto medio)
MAE = sum(abs(y_pred - y_test) for y_pred, y_test in zip(predictions,data_test_y)) / len(predictions)
#Mean Square Error (error cuadrático medio)
MSE = sum((y_pred - y_test)**2 for y_pred, y_test in zip(predictions, data_test_y)) / len(predictions)
#Root Mean Square Error - error de la raíz cuadrada de la media RMSE
RMSE = MSE ** 0.5
#Standard Deviation of Residuals . Desviación típica de los residuos
SDR = (1 / (len(data_test_y) - 1) * sum((y_test - y_pred) ** 2
for y_pred, y_test in zip(predictions, data_test_y))) ** 0.5
print ('Mean Error: %f' %ME)
print ('Mean Absolute Error: %f' %MAE)
print ('Mean Square Error: %f' %MSE)
print ('Root Mean Square Error: %f' %RMSE)
print ('Standard Desviation of Residuals: %f' %SDR)
Mean Error: 0.552777 Mean Absolute Error: 12.685615 Mean Square Error: 254.281254 Root Mean Square Error: 15.946199 Standard Desviation of Residuals: 15.964559
Y calculamos el coeficiente de correlación, R2, que nos dará una idea de la dependecia de las variables, al ser una medida de la relación entre ellas.
data_test_mean = sum(ele
for ele in data_test_y) / len(data_test_y)
predictions_mean = sum(ele
for ele in predictions) / len(predictions)
data_test_std = (1 / (len(data_test_y) - 1) * sum((ele - data_test_mean) ** 2
for ele in data_test_y)) ** 0.5
predictions_std = (1 / (len(predictions) - 1) * sum((ele - predictions_mean) ** 2
for ele in predictions)) ** 0.5
cov = sum([i * j
for (i, j) in zip([ele - data_test_mean
for ele in data_test_y],
[ele - predictions_mean
for ele in predictions])
]) / (len(predictions))
print('El coeficiente de correlación es: R2 = %f' % (cov * * 2 / (data_test_std * * 2 * predictions_std * * 2)))
El coeficiente de correlación es: R2 = 0.810380
Se deduce que el porcentaje de relación entre las variables que puede explicarse mediante nuestro modelo lineal es del 81,03%.
También vamos a comprobar si los errores se reparten según una distribución normal, lo que nos da una prueba de la validez de nuestro modelo.
#Distribución de los Residuos sns.distplot((np.asarray(data_test_y) - np.asarray(predictions)), bins = 50) plt.show()

python scikit-learn
1.- Importamos las librerías necesarias y obtenemos los datos que vamos a necesitar para nuestro modelo de regresión lineal simple.
import pandas as pd import numpy as np import seaborn as sns import matplotlib.pyplot as plt from sklearn.model_selection import train_test_split from sklearn.linear_model import LinearRegression from sklearn import metrics import random import math
Pasamos los datos a un dataframe:
slr_df = pd.read_csv('data_LR.csv', sep="|")
slr_df = df.replace(',','.', regex=True).astype(float)
2.- Echamos un vistazo a los datos.
slr_df.head()
OUTDOOR_TEMP ELECTRIC_POWER 0 30.248541 NaN 1 31.321108 324.54 2 32.704262 NaN 3 24.938467 252.70 4 33.316906 331.10
Aquí ya vemos que tenemos dos valores NaN.
slr_df.describe()
OUTDOOR_TEMP ELECTRIC_POWER count 1496.000000 1494.000000 mean 28.544429 286.214465 std 6.364375 41.516466 min 0.000000 0.000000 25% 26.204395 261.550000 50% 29.232194 288.620000 75% 32.470816 315.852500 max 38.310135 391.710000
slr_df.info()
<class 'pandas.core.frame.DataFrame'> RangeIndex: 1496 entries, 0 to 1495 Data columns (total 2 columns): OUTDOOR_TEMP 1496 non-null float64 ELECTRIC_POWER 1494 non-null float64 dtypes: float64(2) memory usage: 23.5 KB
print('_'*30 + 'NULL VALUES')
slr_df.isnull().sum()
______________________________NULL VALUES OUTDOOR_TEMP 0 ELECTRIC_POWER 2 dtype: int64
Nos cargamos los valores NaN:
slr_df = slr_df.dropna()
3.- Exploramos los datos.
Vamos a hacerlo de forma gráfica.
sns.jointplot(data = slr_df, x = 'OUTDOOR_TEMP', y ='ELECTRIC_POWER')

Eliminar los valores de temperatura exterior iguales a cero, ya que se deben a errores en la medida del sensor.
slr_df = slr_df[slr_df.OUTDOOR_TEMP != 0]
Y volvemos a dibujar
sns.jointplot(data = slr_df, x = 'OUTDOOR_TEMP', y ='ELECTRIC_POWER')
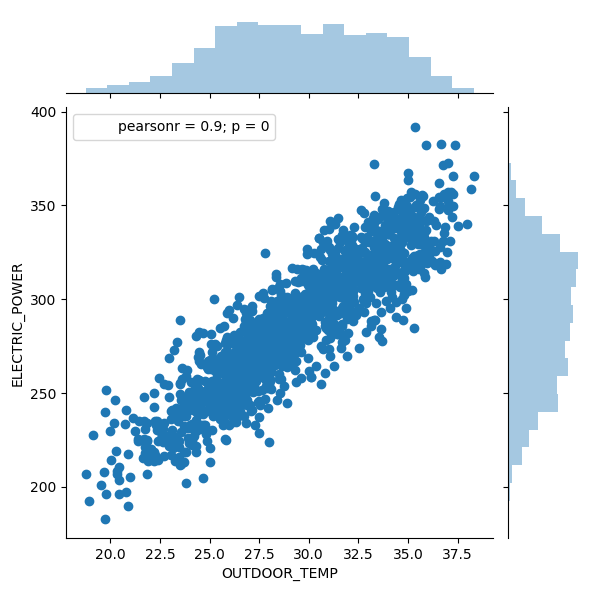
Podemos ver también la densidad de puntos.
sns.jointplot(data = slr_df, x = 'OUTDOOR_TEMP', y ='ELECTRIC_POWER', kind = 'hex')
 Y dibujar un pairplot, aunque solo tengamos dos variables.
Y dibujar un pairplot, aunque solo tengamos dos variables.
sns.pairplot(slr_df)
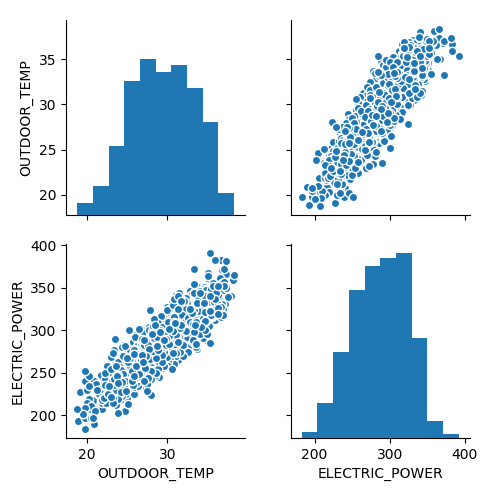
Y la nube de puntos con la recta de regresión.
sns.lmplot(data = slr_df, x = 'OUTDOOR_TEMP', y ='ELECTRIC_POWER')
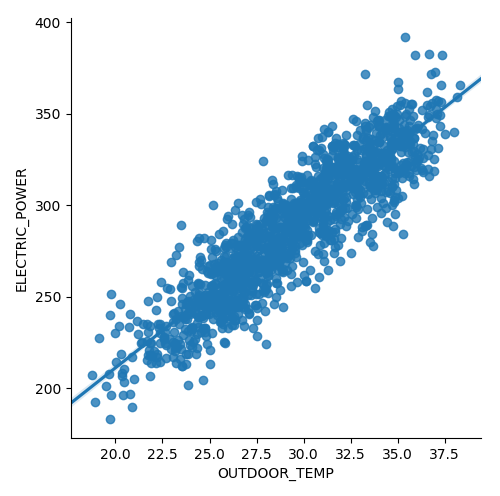
4 .- Creamos los datos de entrenamiento y testeo.
En primer lugar, creamos una variable X con los datos de la temperatura exterior, y una variable y con los datos de la potencia eléctrica.
X = slr_df['OUTDOOR_TEMP'].values.reshape(-1,1) y = slr_df['ELECTRIC_POWER'].values.reshape(-1,1)
Ahora usaremos la función train_test_split del módulo model_selection de sklearn, para crear los datos de entrenamiento y testeo. Para el tamaño de los datos de testeo elegiremos un 30% de los datos totales.
X_train, X_test, y_train, y_test = train_test_split(X, y , test_size=0.3, random_state=10)
5.- Creamos el modelo y lo entrenamos.
Usaremos el modelo LinearRegression del módulo linear_model de sklearn.
Creamos una instancia del modelo:
lm = LinearRegression()
Y lo entrenamos con los datos de entrenamiento:
lm.fit(X_train, y_train)
Le pedimos al modelo la pendiente y el término independiente de la recta:
slope = lm.coef_
intercept = lm.intercept_
print ('La recta de regresión es: y = %f + %f * X'%(lm.intercept_, slope))
La recta de regresión es: y = 48.078355 + 8.149359 * X
Prácticamente a la recta obtenida con el modelo ‘cincel y martillo’.
6.- Hacemos la predicción con los datos de test.
predictions = lm.predict(X_test)
Dibujamos los datos de la predicción frente a los reales:
plt.scatter(y_test, predictions, c='g', edgecolors=(0, 0, 0), alpha=0.5)
plt.title('predicted values vs test values', fontsize=10)
plt.xlabel('test values')
plt.ylabel('predicted values')
plt.show()
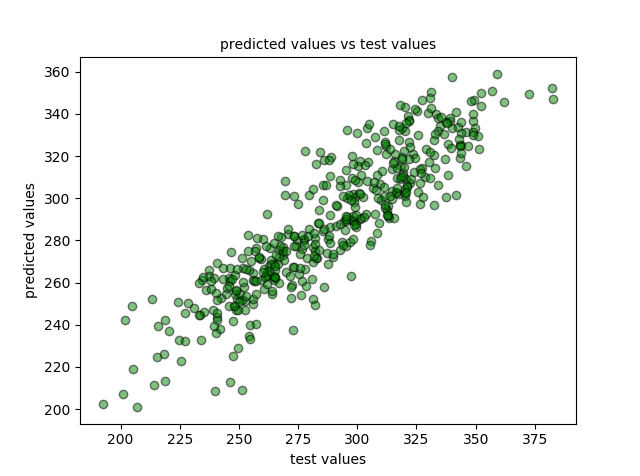
7.- Evaluación del modelo.
Calculamos las mismas metricas que calculamos para nuestro modelo ‘cincel y martillo’, pero esta vez utilizando el módulo metrics de sklearn.
print('MAE: ', metrics.mean_absolute_error(y_test, predictions))
MAE: 12.731898625424554
El MAE que obtuvimos en ‘cincel’ dió: 12.685615
print('MSE: ', metrics.mean_squared_error(y_test, predictions))
MSE: 251.41283940615156
El MSE obtenido en ‘cincel’ fué: 254.28125401950533
print('RMSE: ', np.sqrt(metrics.mean_squared_error(y_test, predictions)))
RMSE: 15.856003260789006
El RMSE obtenido en ‘cincel’ fué: 15.946198732597852
print ('explained_variance_score', metrics.explained_variance_score(y_test, predictions))
print ('r2_score', metrics.r2_score(y_test, predictions)
explained_variance_score 0.8068705820651054 r2_score 0.8068238090094082
El R2 que calculamos en ‘cincel’ fué: 0.810380
Vamos a dibujar el histograma de los residuos para comprobar que tienen una distribución normal:
sns.distplot((y_test - predictions), bins = 50) plt.show()
 Ambos modelos funcionan de forma similar, con unas métricas muy parecidas, y consiguen explicar alrededor de un 80% de la varianza de los datos. Sin ser una maravilla, son valores aceptables.
Ambos modelos funcionan de forma similar, con unas métricas muy parecidas, y consiguen explicar alrededor de un 80% de la varianza de los datos. Sin ser una maravilla, son valores aceptables.